Structure secondaire - Définition
La liste des auteurs de cet article est disponible ici.
Alignement
Les alignements multiples de séquences d'ARN et de protéines peuvent s'appuyer sur la connaissance de leurs structures secondaires. L'inclusion de cette information supplémentaire, quand elle est connue, permet d'améliorer sensiblement la qualité des alignements de séquences.
Dans les protéines, les insertions et délétions dans l'alignement sont en général observées au niveau des boucles et des régions en pelote, mais pas dans les hélices et les feuillets.
Dans les ARN, les appariements de bases sont en général plus conservés que la nature des bases elles-mêmes. Ainsi par exemple, on pourra trouver une paire A-U remplacée par une paire G-C dans un autre ARN homologue. La structure secondaire, sinon la séquence, est ainsi conservée et son identification est essentielle à la construction d'un alignement correct.
Acides nucléiques
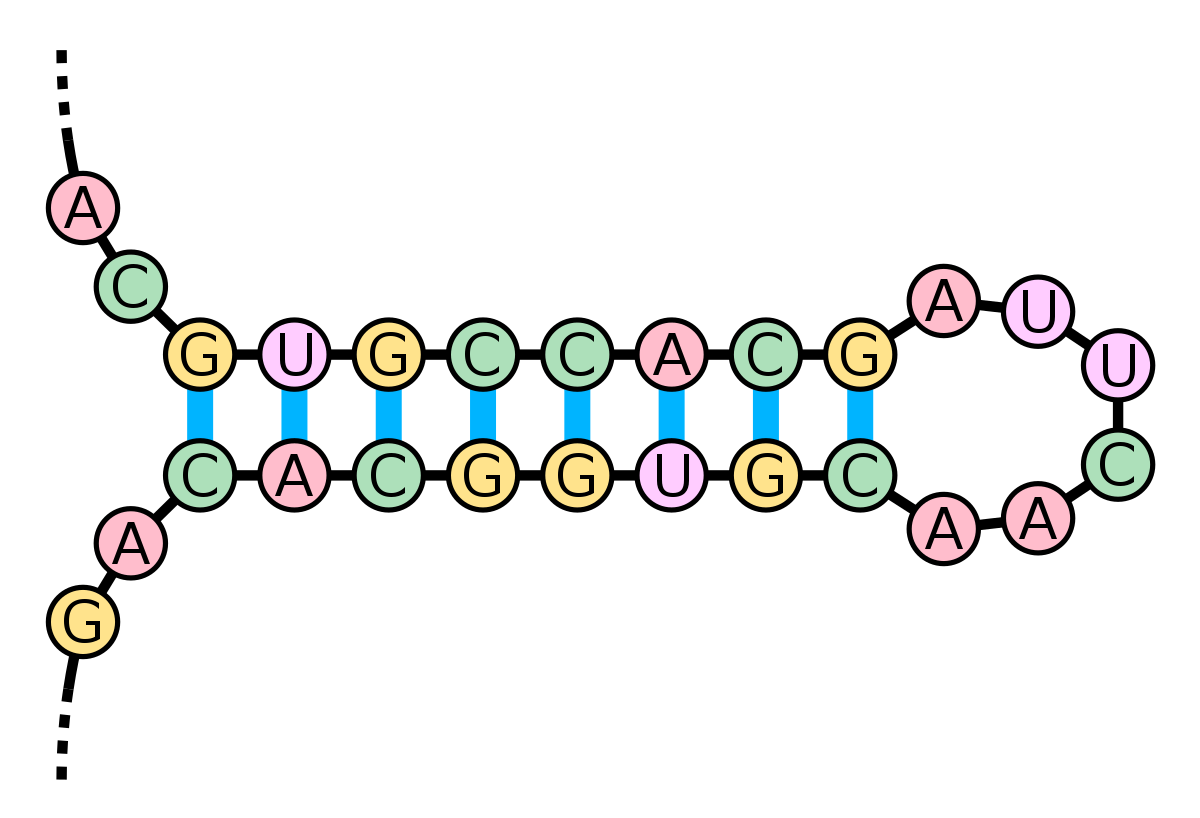
Les acides nucléiques ont aussi une structure secondaire, principalement les ARN simple-brin. La structure secondaire des ARN est divisée en hélices (paires de bases contiguës) et divers types de boucles (nucléotides non-appariés, entourés d'hélices). La structure en "tige et boucle" dans laquelle une hélice appariée se termine par une courte boucle de nucléotides non-appariés est particulièrement fréquente et constitue une brique élémentaire pour former des motifs structuraux plus complexes, comme par exemple la structure en feuille de trèfle des ARNt, où quatre hélices sont associées au niveau d'un jonction centrale. Les boucles internes (une série de nucléotides non appariées au milieu d'une hélice plus longue) et les hernies (régions où l'un des deux brins de l'hélice présente des nucléotides supplémentaires non-appariés avec le brin complémentaire) sont également très courantes. Enfin on peut observer des structures de type pseudonœud et des triplets de bases dans certains ARN.
Dans la mesure où la structure secondaire des ARN repose principalement sur la formation d'appariements de bases, celle-ci peut se définir en identifiant quels nucléotides sont appariés avec lesquels dans une molécule ou dans un complexe. Cependant les appariements canoniques de type Watson-Crick ne sont pas les seuls rencontrés, même si ce sont de loin les plus fréquents. On peut trouver des appariements bancals G-U et d'autres types de paires non canoniques (appariement Hoogsteen, en cisaille...).
Prédiction de structure d'ARN
Pour beaucoup de molécules d'ARN, la structure secondaire est essentielle à leur fonction biologique, souvent plus que leur séquence en nucléotides. Ce point constitue un atout important pour l'analyse des ARN non codants, parfois appelés "gènes ARN". La structure secondaire des ARN peut être prédite avec certaine fiabilité par ordinateur et de nombreuses applications bio-informatiques reposent sur l'utilisation de ces techniques pour l'analyse des ARN.
La méthode générale pour la prédiction de structures secondaires d'ARN repose sur la programmation dynamique. Ces méthodes sont fondées sur des calculs des enthalpies libres associées à la formation des diverses paires de bases, tabulées à partir des paramètres de stabilité thermodynamique de petits fragments d'ARN, mesurée grâce à l'effet hyperchrome. Cette approche ne permet cependant pas de détecter les structures non canoniques et les pseudonœuds.