Protéasome - Définition
La liste des auteurs de cet article est disponible ici.
Assemblage
L'assemblage du protéasome est un processus complexe de par le nombre de sous-unités qui doivent s'associer afin de former un complexe actif. Les sous-unités β sont synthétisées avec un "propeptide" N-terminal qui sera modifié pendant l'assemblage du complexe 20S afin d'exposer le site actif protélytique. 20S est alors assemblé à partir de deux demi-protéasomes, chacun constitué d'un proto-anneau β à sept constituants et attaché à un heptamère α.
L'association des deux anneaux β déclenche une autolyse thréonine-dépendante des propeptides, exposant ainsi le site actif. Ces interactions entre β sont essentiellement le fait de ponts salins et d'interactions hydrophobes entre des hélices alpha conservées (leur mutation diminue la faculté d'assemblage du protéasome). L'association des demi-protéasomes est initiée par le regroupement des sous-unités α en heptamère. Le mode d'assemblage de ces dernières n'a pas encore été caractérisé.
On connaît en général beaucoup moins le mode d'assemblage et de maturation du complexe régulateur 19S. Les sous-unités pourraient s'assembler en deux composants distincts, une base d'ATPases et un chapeau ubiquitine-spécifique. Les six ATPases s'assembleraient en paires par le biais d'interactions coiled coil. L'ordre dans lequel les 19 sous-unités du complexe régulateur s'assemblent est probablement lié à un mécanisme empêchant l'exposition du site actif tant que le mécanisme de régulation n'est lui-même pas en place.
Structure et organisation
Les composants du protéasome sont nommés d'après leur coefficient de sédimentation de Svedberg (noté S). La forme la plus répandue est le protéasome 26S de masse moléculaire 2000 kilodaltons et qui contient un cœur catalytique en forme de baril, le 20S, et deux complexes régulateurs 19S placés de chaque côté de celui-ci.
Le centre est creux et forme la cavité au cœur de laquelle les protéines sont dégradées, après être entrées par l'une des deux extrémités, celle-ci s'associant avec une sous-unité régulatrice 19S contenant des site actif d'ATPase et des sites de liaison avec l'ubiquitine. Cette structure reconnaît les protéines polyubiquitinées et les transfert au centre catalytique. Une autre sous-unité (11S) peut également s'associer avec celui-ci, de la même manière que le ferait un complexe 19S: il a été postulé que 11S jouerait alors un rôle dans la dégradation de peptides "étrangers", tels que ceux produits lors de l'infection par un virus.
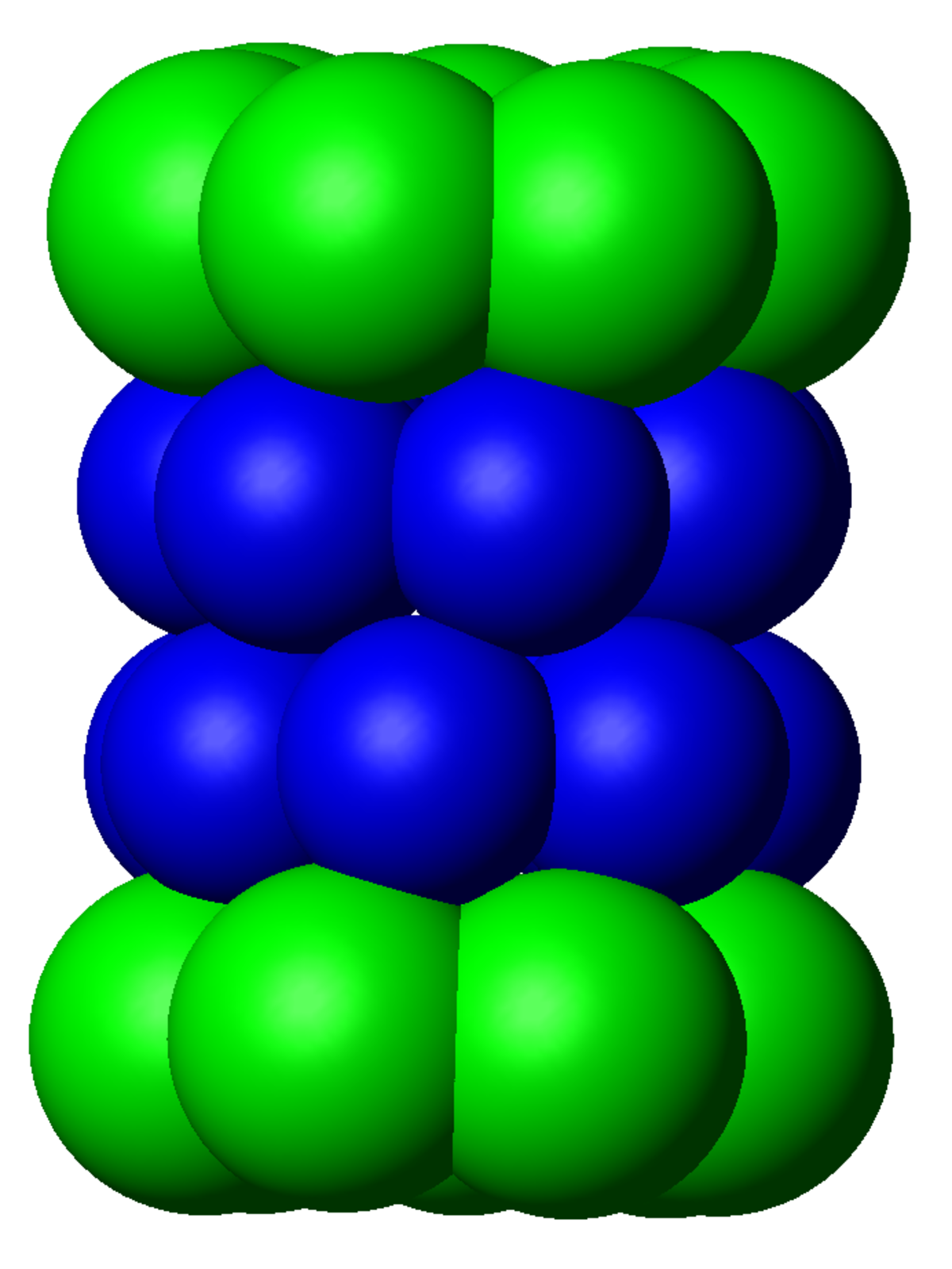
Cœur catalytique 20S
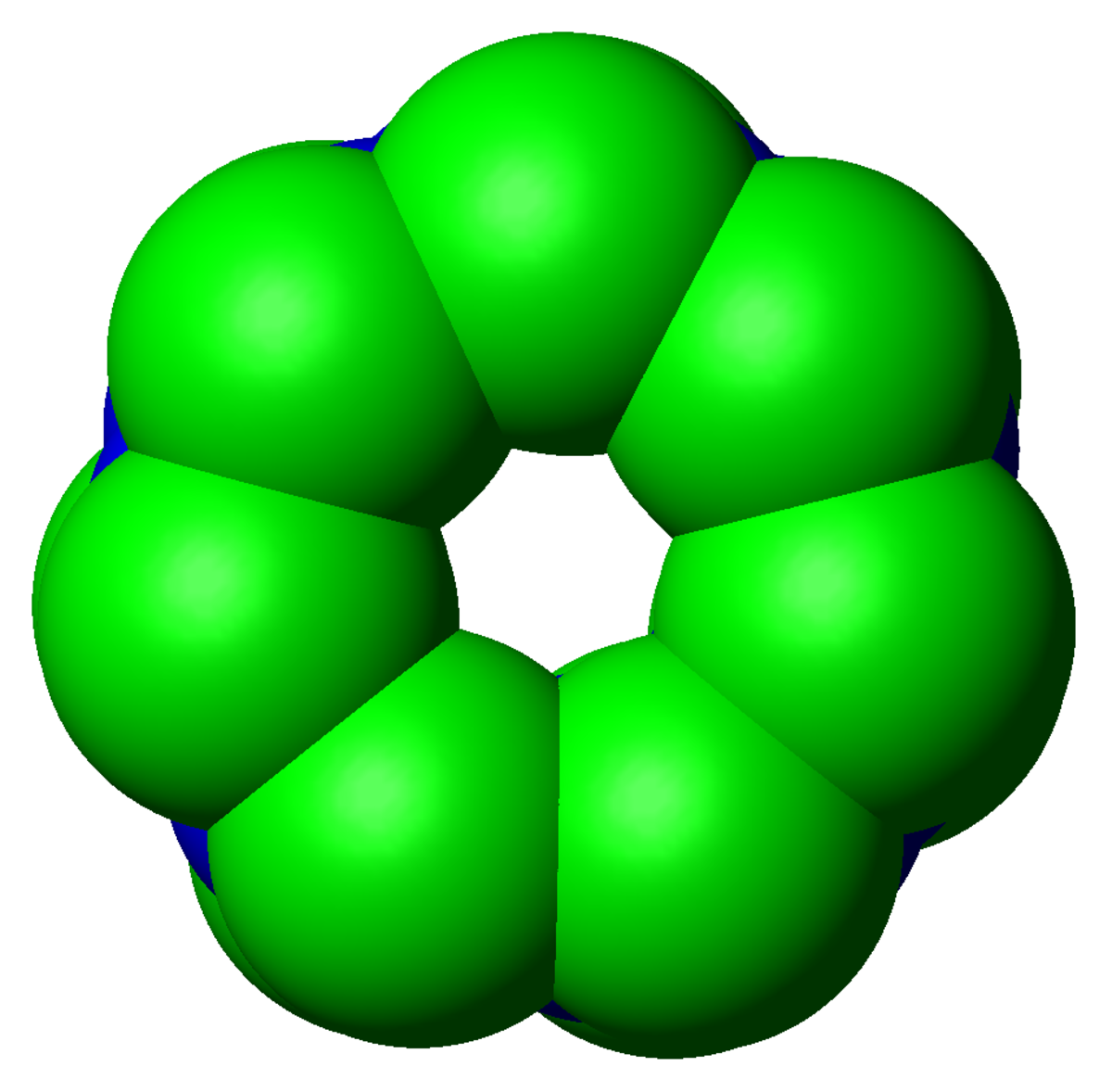
Le nombre et la variété des sous-unités constituant le complexe 20S dépend de l'organisme dont il fait partie, étant entendu que le nombre de sous-unités distinctes et leur degré de spécialisation est plus grand chez les pluricellulaires que chez les unicellulaires, ainsi que chez les eucaryotes par rapport au procaryotes. Cependant, tous les 20S sont constitués de quatre structures heptamériques circulaires, elles-mêmes composée de deux types distincts de sous-unités: les deux anneaux extérieurs de sous unités α servent pour la régulation et ont un rôle plutôt structural (régulation de l'accès des protéines au cœur du protéasome), tandis que les sept sous-unités β des deux anneaux intérieurs portent l’activité catalytique par le biais des sites actifs des protéases qu'elles contiennent.
La taille du protéasome s'est relativement bien conservée pendant l'évolution, celui-ci mesurant environ 150 angstroms (Å) de long par 115 Å de diamètre. Le centre actif ne fait pas plus de 53 Å, mais il arrive que son chemin d'accès ne dépasse pas les 13 Å de large - il est donc probable que les protéines doivent être déjà partiellement dénaturées pour pouvoir interagir avec les site actif.
Chez les eucaryotes (comme la levure), les sept sous-unités sont toutes différentes les unes des autres, tandis que chez les archées elles sont toutes semblables. Les bactéries, à l'exception de l'ordre Actinomycetales, n’ont pas de protéasome 20S mais un complexe analogue appelé Hs1v avec un site catalytique ouvert. Chez les eucaryotes, seules trois sous-unités β sont actives mais elles ont des spécificités de coupure différentes : de type trypsine pour les acides aminés basiques, chymotrypsine pour les acides aminés aromatiques et caspase pour les acides aminés acides. Chez les mammifères par exemple, ce sont les sous-unités β1, β2, et β5 qui sont catalytiques. Des variantes notées β1i, β2i et β5i peuvent être exprimées dans les cellules hematopoïétiques en réponse à des signaux inflammatoires tels que les cytokines, notamment les interférons gammas. Un protéasome constitué de ces sous-unités est appelé un immunoprotéasome, dont la spécificité de substrat est altérée par rapport à un protéasome "normal".
Complexe régulateur 19S
Le complexe 19S est constitué de 19 protéines distinctes et comporte deux zones : une « base » de 10 protéines se colle à l'anneau α du 20S, et possède l’activité ATPase sur 6 de ses 10 constituants (c'est la présence d'ATP qui permet l'association de 19S et 20S); l’autre partie (9 protéines), forme un « chapeau » plus flexible qui sert de couvercle à l’entrée dans le site catalytique. C’est ce complexe qui reconnaît la chaîne de polyubiquitine. Il participe au dépliement de la protéine ainsi qu'à sa translocation dans le cœur du 20S, et contient également une isopeptidase qui va enlever la chaîne d’ubiquitine de la protéine, bien qu'on ne sache pas ecnore exactement si l'énergie dégagée par l'hydrolyse de l'ATP sert au dépliement, à l'ouverture du canal central ou aux deux.
Les différents constituants du complexe 19S ont leur propre activité de régulation: La gankyrine, une oncoprotéine récemment découverte, est un élément de 19S qui interagit également avec la kinase cycline-dépendanteCDK4, et joue un rôle dans la reconnaissance de la version ubiquitinée de p53 par le biais de son affinité avec l'ubiquitine ligase MDM2. La gankyrine est anti-apoptotique et il a été démontré qu'elle était surexprimée dans certains types de tumeurs tels que le carcinome hépatocellulaire.
Complexe régulateur 11S
Il existe enfin un complexe 11S heptamérique dit « activateur » qui peut s’associer au 20S. Il stimule l’activité peptidase du protéasome mais est incapable de reconnaître l’ubiquitine et ne possède pas d'activié ATPase. Il pourrait jouer un rôle dans la dégradation des peptides viraux, mais pas de protéines plus larges. Cette structure 11S peut parfois être rencontrée sous le terme de PA28 ou REG. Le mécanisme utilisé pour se lier à 20S par le biais de son C-terminus et ouvrir l'accès au cœur du protéasome en favorisant une modification de la conformation des anneaux α semble très proche, sinon similaire, à celui utilisé par le complexe 19S.
L'expression de 11S est induite par l'interféron gamma et, en association avec les sous-unités β de l'immunoprotéasome, provoque la génération de peptides qui iront se lier au complexe majeur d'histocompatibilité.
La structure du complexe 26S n'était toujours pas élucidée en 2006, mais on pense que les complexes 11S et 19S se lient de manière similaire au complexe 20S.