Acide ribonucléique messager - Définition
La liste des auteurs de cet article est disponible ici.
Contrôle qualité des ARNm
Les cellules vivantes ont développé différents mécanisme de contrôle qualité des ARNm. Cela permet suivant les cas de vérifier que l'ARNm est intact et qu'il code bien pour une protéine complète. Ceci évite la production de protéines anormales qui en s'accumulant pourraient finir par tuer la cellule. Ces mécanismes sont différents chez les bactéries et chez les eucaryotes.
Chez les eucaryotes, le principal mécanisme de contrôle qualité est la vérification de la présence de la coiffe et de la queue poly(A). Sans ces éléments, l'ARNm n'est pas exporté du noyau et ne peut être traduit car il n'y a pas formation du pseudo-cercle via l'interaction eIF4E/eIF4G/PABP décrite plus haut. Ainsi, par exemple, si un ARNm est endommagé et subit une coupure chimique ou enzymatique, il ne sera pas traduit, car l'extrémité 5' qui porte la coiffe et l'extrémité 3' qui porte la queue poly(A) seront séparées. Les eucaryotes disposent d'un autre mécanisme de contrôle qualité, le nonsense mediated decay ou dégradation des ARNm non-sens. Ce mécanisme conduit à la dégradation des ARNm qui contiennent un codon-stop prématuré, résultant par exemple d'une mutation dans le génome. C'est le ribosome, lors de la première traduction de l'ARNm, qui semble être le médiateur de ce contrôle.
Chez les bactéries, il existe un mécanisme de contrôle qualité qui permet de débloquer les ribosomes qui sont bloqués sur un ARNm, par exemple lorsqu'il ne contient pas de codon stop. Ceci peut se produire si l'ARNm a été clivé et qu'il manque la partie 3' qui contient la fin du cadre ouvert de lecture et le codon stop. Ce mécanisme fait intervenir un ARN spécifique, l'ARNtm qui permet de débloquer le ribosome, par un mécanisme appelé trans-traduction qui fait changer le ribosome de message en cours de synthèse. La protéine incomplète est ainsi étiquetée par un peptide qui provoque sa dégradation rapide dans la cellule et donc l'accumulation de protéines aberrantes.
Traduction en proteine
Les ARNm maturés sont ensuite traduits en protéines par les ribosomes dans le cytoplasme. La petite sous-unité du ribosome (30S chez les bactéries ou 40S chez les eucaryotes) se fixe d'abord dans la région amont de l'ARNm et glisse jusqu'au codon de démarrage. Cette étape nécessite l'intervention d'un ensemble de protéines spécifiques appelées facteurs d'initiation. Il recrute alors le premier ARN de transfert et la grande sous-unité du ribosome (50S chez les bactéries et 60S chez les eucaryotes) s'associe à l'ensemble. Le ribosome ainsi assemblé démarre la traduction.
A la fin de cette phase d'initiation, les facteurs d'initiation quittent le ribosome assemblé qui va allonger la protéine codée par l'ARNm, au cours de cycles d'élongation successives. A chaque cycle, le ribosome lit un codon et y associe l'ARNt de codon complémentaire, qui porte l'acide aminé correspondant. Cette étape nécessite l'action de facteurs d'élongation. Une fois l'ensemble du cistron lu par le ribosome, celui parvient sur le codon-stop qui le termine. Le ribosome libère la protéine terminée, puis le dernier ARNt et enfin l'ARNm. Ces étapes nécessitent l'intervention de facteurs de terminaison.
Les différentes étapes impliquées sont détaillées ci-après.
Les ARNm dans le cytoplasme
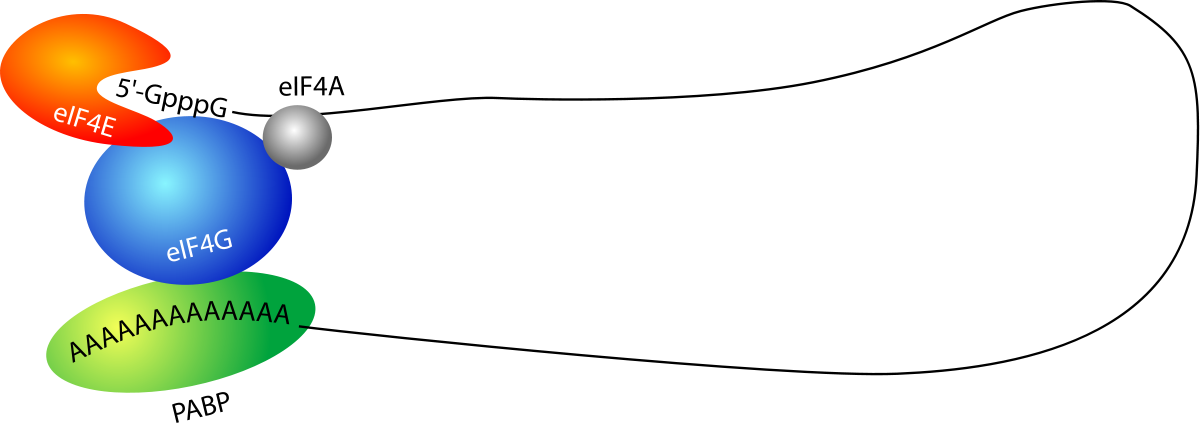
Dans le cytoplasme des cellules eucaryotes, les ARNm existent sous forme de complexes associés à des protéines, sous forme de pseudo-circulaire. La coiffe en 5' est en effet reconnue par le facteur de démarrage de la traduction eIF4E. La queue poly(A) est recouverte par une protéine spécifique, la PABP (poly(A) binding protein). Ces protéines, eIF-4E et PABP interagissent toutes les deux avec une même protéine organisatrice, le facteur de démarrage eIF4G . Ceci conduit à une circularisation de l'ARNm au travers de ce complexe protéique, ses deux extrémités 5' et 3 étant ainsi rapprochées. Ce complexe contient aussi d'autres facteurs de démarrage, comme eIF4A qui est une ARN hélicase.
L'un des effets de la formation de ces complexes circulaires est de permettre la rapprochement du 5'-UTR et du 3'-UTR de l'ARNm. Ces deux régions peuvent contenir des signaux d'expression qui vont ainsi pouvoir jouer conjointement sur le recrutement du ribosome. C'est aussi un moyen pour la cellule de vérifier que l'ARNm est complet et contient bien simultanément une coiffe et une queue poly(A) avant de démarrer la traduction.
Recrutement du ribosome
Le recrutement du ribosome sur l'ARNm est une étape clé de la synthèse des protéines. L'efficacité de cette étape détermine en particulier de taux de synthèse final de la ou des protéines codées par l'ARNm. C'est à ce niveau que s'exercent la plupart des régulations dites "traductionnelles" de l'expression du génome (par opposition aux régulations transcriptionnelles qui affectent le taux de synthèse de l'ARNm). Le mécanisme de recrutement du ribosome est différent chez les eucaryotes et chez les bactéries. Chez ces dernières, la petite sous-unité du ribosome (30S) procède par un mécanisme d'entrée interne sur l'ARNm, directement sur le codon de démarrage. A l'inverse, chez les eucaryotes, la sous-unité 40S est recrutée à l'extrémité 5' de l'ARNm, sur la coiffe, et procède par un mécanisme de balayage (scanning). Enfin, il existe dans certains cas un mécanisme d'entrée interne du ribosome chez les eucaryotes, en particulier chez certains ARNm viraux. Ceux-ci nécessitent des structures particulière sur l'ARNm, appelées IRES.
Démarrage de la traduction procaryote
Chez les bactéries, le démarrage de la traduction des ARNm correspond à la reconnaissance du codon de démarrage. Celui-ci est un codon AUG, GUG ou plus rarement UUG, qui doit être précédé sur l'ARNm par une séquence conservée riche en purine, appelée RBS (Ribosome-binding site) ou séquence de Shine & Dalgarno. Ce RBS est en général séparé du codon de démarrage par 6 à 12 nucléotides. Sa séquence est complémentaire de l'extrémité 3' de l'ARN ribosomique 16S, il se forme ainsi un appariement entre ARNm et ARNr, juste en amont du codon de démarrage qui se trouve ainsi pré-positionné dans le site P, dans la sous-unité 30S ribosome.
La formation du complexe de démarrage fait intervenir trois facteurs d'initiation, appelés IF1, IF2 et IF3. IF1 vient se localiser au niveau du site A de la sous-unité 30S et en bloque ainsi l'accès pendant la phase de démarrage. IF2 s'associe à l'ARNt initiateur portant une formyl-méthionine qui sera le premier acide aminé incorporé dans la protéine. IF3 s'associe à la sous-unité 30S, dont il empêche la réassociation avec la sous-unité 50S.
Le processus se déroule de la manière suivante : la sous-unité 30S associée à IF3 balaie l'ARNm jusqu'à trouver un site RBS auquel elle s'apparie. L'ARNt associé à IF2 rentre dans le site P, canalisé dans ce processus par IF1 qui bloque l'autre site. L'interaction codon-anticodon entre l'ARNm et l'ARNt cale le ribosome sur le bon cadre de lecture. IF2 hydrolyse une molécule de GTP, IF3 et IF1 quittent le complexe. La sous-unité 50S peut alors s'associer. Le ribosome complet peut alors commencer la traduction au niveau du second codon du cistron.
Démarrage de la traduction eucaryote
Chez les eucaryotes, les ARNm matures existent sous forme de complexes pseudo-circulaires dans le cytoplasme (voir plus haut), associant les facteurs de démarrage eIF4E, eIF4G et eIF4A, ainsi que la PABP. C'est le facteur eIF4G qui joue le rôle de protéine organisatrice dans ce complexe car il est lié simultanément à la coiffe via eIF4E et à la queue poly(A) via la PABP. Lorsque ces deux interactions sont réalisées, eIF4G peut effectuer le recrutement de la petite sous-unité (40S) du ribosome.
Cette dernière est elle-même associée à plusieurs facteurs au sein d'un complexe de pré-initiation 43S. Celui-ci contient, outre la sous-unité ribosomique 40S, l'ARNt de démarrage aminoacylé par la méthionine associé au facteur eIF2 complexé au GTP, le facteur eIF3 qui maintient la sous-unité 40S dissociée de la grande sous-unité, ainsi que eIF1A et eIF5. Au sein de ce complexe de pré-initiation, eIF3 interagit avec eIF4G au sein du complexe ARNm. Ceci permet le recrutement du ribosome au niveau de la coiffe de l'ARNm. Le complexe d'initiation complet ainsi formé est appelé complexe 48S. Il contient donc :
- l'ARNm coiffé et polyadénylé ;
- la sous-unité 40S du ribosome ;
- l'ARNt de démarrage au site P de la précédente. Cet ARNt est aminoacylé par la méthionine et associé à eIF2:GTP ;
- les facteurs de démarrage eIF1, eIF1A, eIF2 (déjà cité), eIF3, eiF4A, eIF4B, eIF4E, eIF4G et eIF5.
Ce complexe 48S, recruté sur la coiffe de l'ARNm va alors avancer le long de l'ARNm jusqu'à atteindre le premier triplet AUG qui va être reconnu comme codon d'initiation. Cette reconnaissance est renforcée par la présence de nucléotides conservés autour du codon AUG qui renforcent l'interaction avec le ribosome. Ce consensus est appelé séquence de Kozak. Il se forme alors une interaction entre l'anticodon de l'ARNt et ce codon AUG. Ceci permet de caler le ribosome sur le cadre de lecture du gène. Ce "balayage" de l'ARNm par le ribosome est facilité par l'activité hélicase de eIF4A qui, avec eIF4B, va ouvrir les structures secondaires éventuelles présentes dans le 5'-UTR. Une fois le codon de démarrage reconnu et l'interaction codon-anticodon formée, Il y a hydrolyse du GTP par eIF2, dissociation des facteurs de démarrage et recrutement de la sous-unité 60S. Le ribosome assemblé peut alors commencer la synthèse de la protéine.
Démarrage de la traduction dépendant des IRES
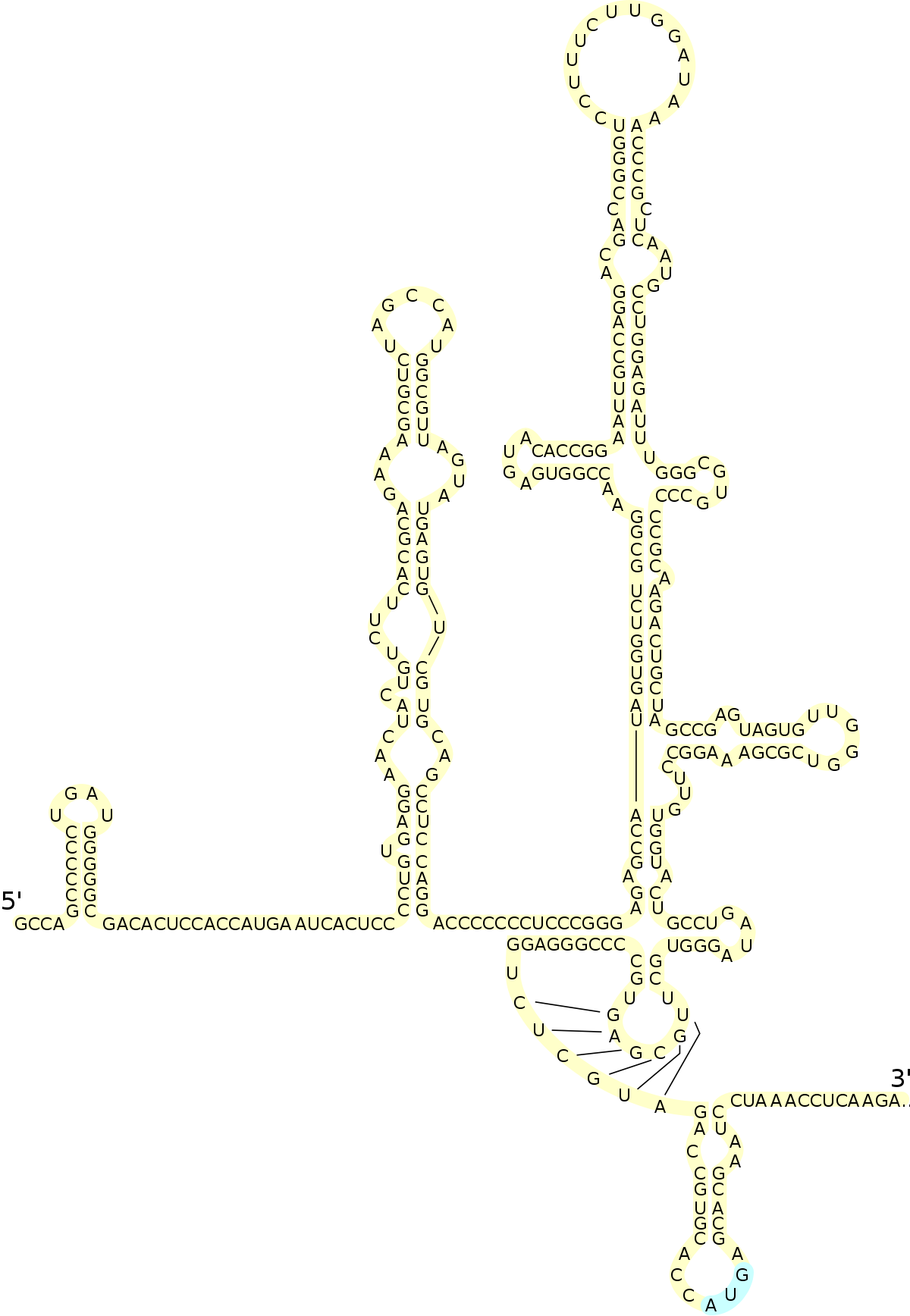
Les IRES (pour internal ribosome entry site) sont des régions structurées de la région 5'-UTR des ARNm qui permettent le recrutement direct du ribosome, indépendamment de la coiffe en 5' et de certains des facteurs de démarrage de la traduction. Ces IRES sont principalement utilisés par des virus qui détournent la machinerie de traduction de la cellule infectée à leur profit. En général, le virus produit une enzyme capable d'inactiver un ou plusieurs des facteurs de démarrage classique, par exemple eIF4G, ce qui abolit la traduction de tous les ARNm cellulaires endogènes. L'ARNm viral utilise alors son IRES pour recruter le ribosome, ce qui lui permet d'être le seul à être traduit dans la cellule. Ce mécanisme a été identifié pour la première fois chez le poliovirus.
Les IRES correspondent à des régions de structure secondaire de l'ARNm, ce qui leur permet d'adopter un repliement tridimensionnel complexe. Cette structure complexe forme alors des interactions spécifiques avec certains facteurs de traduction ou directement avec le ribosome. Ceci permet de court-circuiter le mécanisme classique de recrutement du ribosome via la coiffe en 5'. Ainsi, par exemple, le virus de l'hépatite C possède un IRES dans sa région 5'-UTR qui recrute directement eIF3, sans nécessiter l'intervention de eIF4E et eIF4G. Il existe une grande variété d'IRES, qui permettent de se passer de plus ou moins de facteurs de démarrage cellulaires.
On a également rapporté l'existence d'IRES permettant l'expression de gènes cellulaires, comme c-myc, même si la fonctionnalité de ces IRES reste discutée.
Elongation
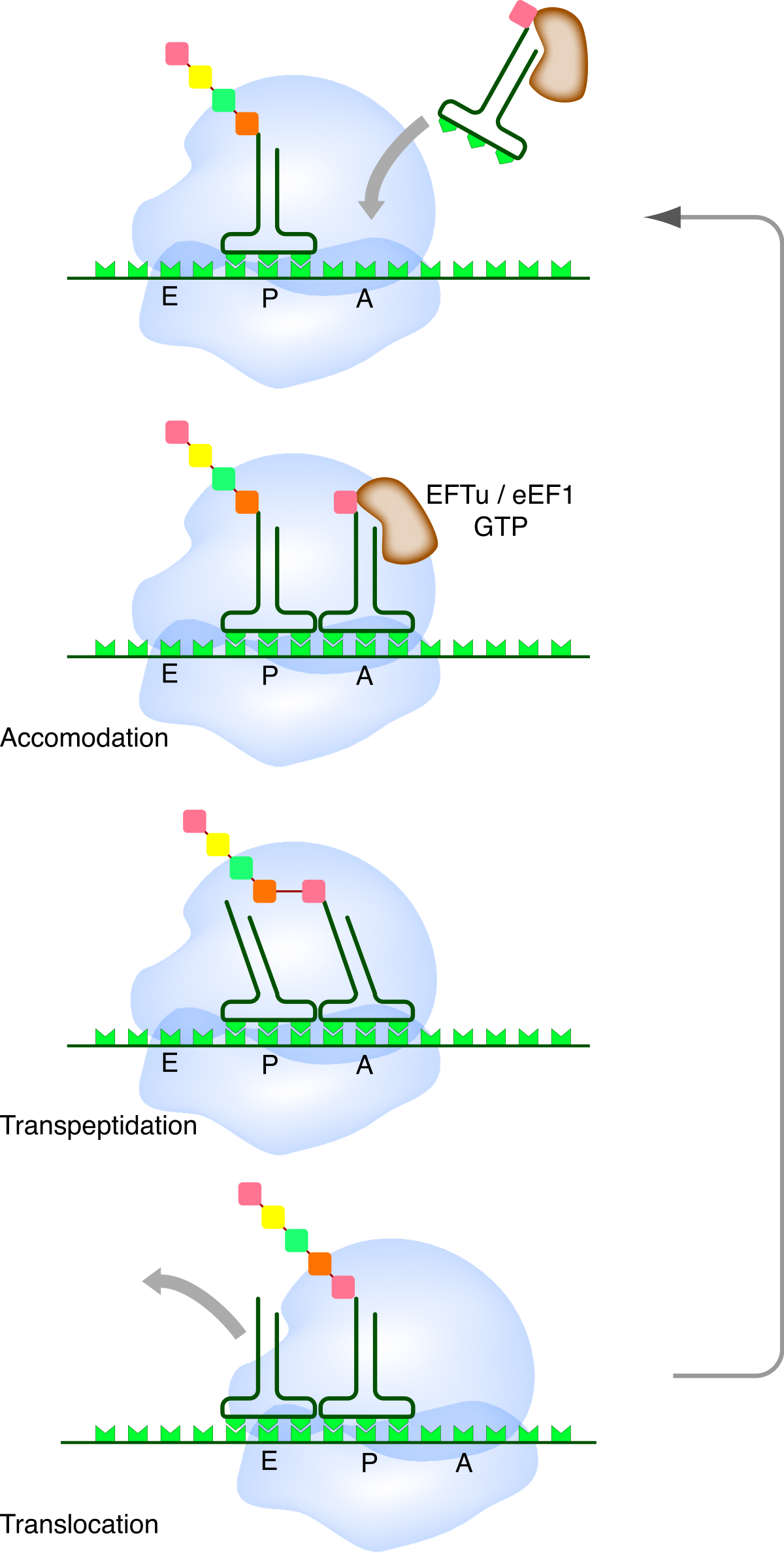
Au cours de la phase d'élongation, l'ARNm traverse le ribosome au niveau d'un sillon de la petite sous-unité. Pendant ce processus, un ou plusieurs ARN de transfert sont associés à l'ARNm au niveau de trois sites présents dans le ribosome.
- site A pour site Aminoacyl-ARNt. Ce site accueille les ARNt portant l'acide aminé qui va être ajouté à la chaîne. C'est au niveau du site A que s'effectue le décodage de l'information génétique, grâce à la reconnaissance de l'interaction entre le codon sur l'ARNm et l'anticodon sur l'ARNt ;
- site P : pour site Peptidyl-ARNt. Ce site accueille l'ARNt qui porte la chaîne peptidique déjà synthétisée. Ce dernier est toujours apparié à l'ARNm par son anticodon ;
- site E ou site de sortie (en: exit). Ce site accueille l'ARNt "nu" après transfert de la chaîne peptidique sur l'ARNt suivant, juste avant qu'il ne quitte le ribosome ;
Ces trois sites sont occupés séquentiellement par les ARNt au fur et à mesure de la progression du ribosome sur l'ARNm. A tout instant du processus de traduction, au plus deux de ces trois sites sont occupés simultanément : soit le site P et le site A, soit le site E et le site P.
Le début du cycle de synthèse démarre avec le ribosome ayant un seul ARNt fixé au site P par l'interaction codon-anticodon. Celui-ci porte estérifié à son extrémité 3' le début de la chaîne peptidique synthétisée. Le site A est initialement vacant. Des ARNt aminoacylés diffusent dans le ribosome de manière stochastique. Ceux-ci sont associés à un facteur d'élongation (ET-Tu chez les bactéries, eIF-1 chez les eucaryotes) qui est une GTPase. Le ribosome teste si l'appariement codon-anticodon est correct. Si il ne l'est pas l'ARNt est rejeté et le processus d'essai-erreur se répète. Lorsqu'un ARNt correct s'apparie enfin au codon, le facteur d'élongation hydrolyse une molécule de GTP, ce qui provoque un changement de conformation du complexe ribosomique et la dissociation du facteur d'élongation. Il y a alors formation de la liaison peptidique entre l'acide aminé porté par l'ARNt au site A et celui porté par l'ARNt au site P. Cette réaction se produit au niveau du site catalytique de la grande sous-unité du ribosome et conduit au transfert de la chaîne peptidique sur l'ARNt lié au site A. Le ribosome recrute alors un facteur de translocation (EF-G chez les bactéries, eEF-2 chez les eucaryotes), lui aussi lié à une molécule de GTP. Ce facteur utilise l'énergie d'hydrolyse de ce GTP pour permettre la progression du ribosome sur l'ARNm. L'ARNt nu qui était au site P se retrouve décalé au site E de sortie et l'ARNt qui était au site A vient au site P. Le site A redevient ainsi vacant. L'ARNt nu du site E diffuse en dehors du ribosome et on revient dans l'état initial pour un nouveau cycle d'élongation.
ARN de transfert
Les ARN de transfert ou ARNt sont des molécules adaptatrices qui font l'intermédiaire entre le codon porté par l'ARN messager et l'acide aminé qui sera incorporé dans la protéine en cours de synthèse par le ribosome. A l'une de leurs extrémités se trouve une boucle contenant un triplet de nucléotides, l'anticodon, qui est complémentaire du codon. Cet appariement codon-anticodon permet la reconnaissance de l'ARNt par le ribosome. Du côté opposé à l'anticodon, les ARNt portent un acide aminé attaché par une liaison ester à leur extrémité 3'-OH. Chaque cellule contient un ensemble d'ARNt différents, capables de s'apparier aux différents codons et spécifiques chacun d'un acide aminé donné. Leurs structures sont analogues, il adoptent une structure secondaire en forme de feuille de trèfle qui se replie en trois dimensions pour former une sorte de « L », avec l'anticodon d'un côté et l'acide aminé de l'autre.
Recodage
Le recodage est un évènement programmé, survenant pendant la lecture de l'ARNm par le ribosome et qui modifie le codage initial. La traduction en protéine résultante est donc différente de celle qu'on pourrait déduire à partir du code génétique standard. Il existe deux principaux évènements de recodage, avec des mécanismes distincts : le recodage de codon-stop et le décalage de cadre de lecture.
Le recodage de codon-stop permet à la cellule d'utiliser un codon stop, en général le codon UGA, pour insérer un acide aminé spécifique. Ce mécanisme est en particulier utilisé pour insérer la sélénocystéine dans les sélénoprotéines. La présence du codon UGA ne suffit pas, il faut en plus la présence d'une structure secondaire spécifique sur l'ARNm et l'intervention de facteurs protéiques dédiés.
Le décalage du cadre de lecture est un mécanisme utilisé en particulier par les virus. Dans certaines conditions, le ribosome peut en effet "déraper" et glisser d'un nucléotide sur l'ARNm, ce qui permet de modifier la nature de la protéine synthétisée. Ce mécanisme est par exemple utilise par le virus du SIDA pour produire les différentes enzymes nécessaires à sa réplication.
Ces décalages du cadre de lecture se produisent à des sites précis, au niveau d'une séquence "glissante", composée d'un nucléotide répété, comme par exemple AAAAAAA. Cette séquence est en général suivie d'une structure secondaire stable sur l'ARNm, souvent un pseudonœud. Le ribosome est gêné dans sa progression par cette structure, ce qui provoque une pause dans la traduction. Pendant cette pause, il y a un codon AAA au site P du ribosome et un codon AAA au site A. Le ribosome en pause peut alors reculer d'un nucléotide en conservant ses deux ARNt fixés. Les appariements entre les codons et les anticodons (AAA / UUU) sont conservés, du fait de la nature particulière de la séquence glissante. La traduction continue alors sur une phase décalée. Ce glissement ne s'effectue pas à chaque traduction, mais avec une fréquence qui dépend de l'environnement et de la structure secondaire sur l'ARN messager. Ainsi le virus (ou la cellule) peut produire deux protéines distinctes à partir d'un seul ARNm.
Terminaison de la traduction
La terminaison de la traduction des protéines est le processus qui permet la libération de la protéine terminée une fois tout le gène lu par le ribosome, ainsi que le recyclage des différents acteurs impliqué, à savoir les sous-unités du ribosome, l'ARNm et le dernier ARNt. Comme l'initiation et l'élongation, cette étape fait intervenir des protéines spécifiques, appelées facteurs de terminaison de la traduction (RF ou eRF, pour release factors). La terminaison est déclenchée par l'arrivée d'un codon-stop dans le site A du ribosome. A ce stade, la protéine complète est encore accrochée par une liaison ester au dernier ARNt situé au site P. Il n'existe normalement pas d'ARNt portant un anticodon complémentaire du codon-stop et pouvant se lier à l'ARNm au site A. A la place, un premier facteur de terminaison (RF1 ou RF2 chez les bactéries et eRF1 chez les eucaryotes) se lie au ribosome et interagit avec le codon-stop. Ceci déclenche l'hydrolyse de la liaison ester entre la protéine et le dernier ARNt. La protéine ainsi libérée quitte le ribosome. Un second facteur (RF3 ou eRF3) qui est une GTPase se lie alors au ribosome, l'hydrolyse du GTP permettant alors le départ des deux facteurs. L'ARNt et le l'ARNm sont finalement libérés par l'action de RRF (ribosome release factor) et de facteurs d'élongation et d'initiation (EF-G et IF3 chez les bactéries).
Régulation de la traduction
Le contrôle de l'expression des gènes peut se faire au niveau de la traduction de l[ARN en protéine. Ce type de régulation agit principalement au niveau de l'étape de démarrage de la traduction par le ribosome. Plus rarement, c'est au niveau de la phase d'élongation ou de terminaison de la traduction qu'on peut avoir un contrôle. En modulant l'efficacité du recrutement du ribosome au niveau du codon de démarrage, la cellule contrôle la quantité de protéine qui est produite à partir de l'ARNm.
Dans de nombreux cas, ces mécanismes impliquent des structures spécifiques sur l'ARNm dont la traduction est régulée. La régulation peut faire intervenir un régulateur traductionnel exogène qui peut être soit une protéine, soit un autre ARN qui interfère avec la traduction par le ribosome en réponse à un signal extérieur (concentration d'un métabolite, température, présence d'un facteur protéique...). Ce régulateur peut être un activateur ou un répresseur, comme dans le cas de la régulation de la transcription.
La régulation de la traduction se passe dans le cytoplasme de la cellule, où se déroule cette étape de l'expression des gènes, tandis que la régulation de la transcription a lieu dans le noyau (chez les cellules eucaryotes).
Fidélité de la traduction
Le processus de traduction de l'ARNm en protéine a un taux d'erreur qui est de l'ordre de 10-4, soit un acide aminé incorrect sur 10000 acides aminés incorporés. La fidélité du mécanisme de traduction de l'ARNm par le ribosome repose sur deux étapes clés importantes. Il faut tout d'abord que chaque ARNt porte le bon acide aminé estérifié à son extrémité 3', une étape qui est réalisée par une famille d'enzyme, les aminoacyl-ARNt synthétases. Les aminoacyl-ARNt synthétases ont souvent une fonction de relecture ou proofreading, comme les ADN polymérases, qui leur permet de vérifier que le produit de leur réaction est bien correct et sinon de l'hydrolyser. L'autre étape critique est la vérification de l'interaction codon-anticodon par le ribosome, une étape qui est aussi soumise à un processus de relecture, assisté par le facteur d'élongation de la traduction EF-Tu.